HELIOPOLIS BIOTECH – Proteindesign, Antikörperdesign
Dieses Tool bewerten
Durchschnittsbewertung
Gesamtstimmen
Wähle deine Bewertung (1-10):
Detailinformationen
Was
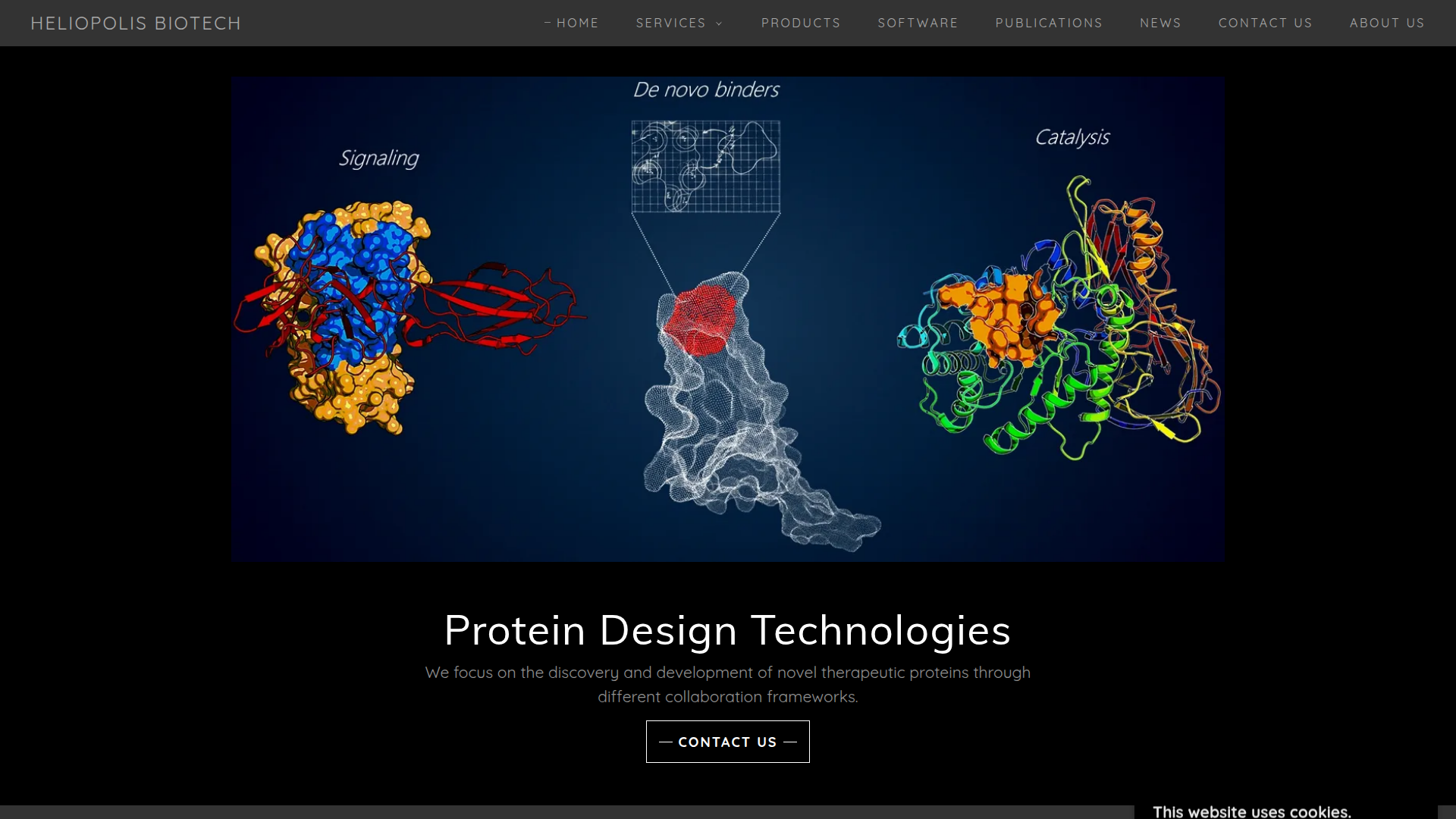
HELIOPOLIS BIOTECH ist ein Protein-Engineering-Unternehmen mit Schwerpunkt auf der computergestützten und experimentellen Entdeckung neuartiger therapeutischer Proteine. Die Website stellt das Unternehmen als Partner für Wirkstoffforschungsteams und Forschungsorganisationen dar, die kundenspezifisches Proteindesign, Binder-Design oder die Neugestaltung bestehender Proteine für therapeutische Anwendungen benötigen.
Der Workflow scheint computergestützte Designalgorithmen mit experimenteller Charakterisierung zu kombinieren, um vom molekularen Konzept bis zum präklinischen Kandidaten zu gelangen. Auf Grundlage der Seite positioniert sich das Unternehmen als spezialisierter Partner für die frühe Entdeckung therapeutischer Proteine und nicht als universelle Softwareplattform.
Funktionen
- De-novo-Proteindesign: Entwickelt Proteine mit neuartigen Faltungen und Sequenzen unter Verwendung fragmentbasierter Methoden, um vorgegebene Rückgratarchitekturen zu erfüllen. Das ist nützlich, wenn bestehende natürliche Proteine nicht zum angestrebten Designziel passen.
- De-novo-Binder-Design: Erzeugt einkettige, hochaffine Binder gegen definierte konformationelle Epitope und unterstützt damit gezielte molekulare Erkennung für therapeutische oder Forschungsanwendungen.
- Protein-Redesign: Überarbeitet bestehende Proteine durch De-novo-Loop-Design und topologische Neuverdrahtung, um Faltungen zu vereinfachen und biophysikalische Eigenschaften zu verbessern.
- Computergestützte Designalgorithmen: Nutzt hauseigene computergestützte Methoden, um molekulare Interaktionen zu steuern und Proteinarchitekturen mit atomarer Präzision zu konstruieren, wodurch Designoptionen vor der experimentellen Arbeit eingegrenzt werden.
- Pipeline zur experimentellen Charakterisierung: Bewertet biophysikalische Eigenschaften, atomare Struktur und pharmakologische Aktivität und liefert damit die Validierungsschritte, die zur Identifizierung stärkerer Kandidaten erforderlich sind.
- Kollaborationsbasiertes Servicemodell: Bietet seine Fähigkeiten über verschiedene Kooperationsmodelle an, was auf einen serviceorientierten Ansatz hinweist, der auf die Discovery-Programme von Partnern zugeschnitten ist.
Hilfreiche Tipps
- Bei dieser Art von Anbieter sollte das Zielproduktprofil früh definiert werden, einschließlich Epitop, Bindungsanforderungen und Developability-Beschränkungen, da die Designqualität stark von den Eingangsspezifikationen abhängt.
- Fragen Sie, wie computergestützte Ergebnisse für die experimentelle Validierung priorisiert werden, da der praktische Erfolg ebenso stark von der Screening-Strategie wie von der Modellerzeugung abhängt.
- Klären Sie, ob das Projektziel Neuartigkeit, Affinität, Stabilität, Herstellbarkeit oder Faltungsvereinfachung ist, da jede Service-Linie offenbar auf ein anderes Discovery-Problem optimiert ist.
- Wenn Sie Anbieter bewerten, achten Sie auf Nachweise dafür, wie die experimentelle Charakterisierung an die präklinische Übergabe anknüpft, da die Seite zwar einen beschleunigten Übergang zu präklinischen Kandidaten angibt, auf dieser Seite jedoch nur begrenzte Prozessdetails liefert.
- Betrachten Sie dies als spezialisierten Discovery-Partner und nicht als Self-Service-Softwareprodukt, da die Seite Dienstleistungen und Zusammenarbeit stärker betont als den Zugriff auf eigenständige Tools.
OpenClaw-Fähigkeiten
Innerhalb des OpenClaw-Ökosystems könnte HELIOPOLIS BIOTECH wahrscheinlich Agenten-Workflows zur Orchestrierung der Entdeckung therapeutischer Proteine unterstützen. OpenClaw-Fähigkeiten könnten beispielsweise dabei helfen, Target-Briefs zu strukturieren, Literatur zu konformationellen Epitopen zusammenzufassen, Kandidaten-Designstrategien zwischen De-novo-Design- und Redesign-Pfaden zu vergleichen und Entscheidungsprotokolle über computergestützte und experimentelle Phasen hinweg zu verwalten. Dabei handelt es sich wahrscheinlich eher um Workflow-Erweiterungen als um bestätigte native Integrationen, da die Seite keine APIs oder Plattformkonnektivität erwähnt.
Ein fortgeschritteneres OpenClaw-Setup könnte Teams aus Business Development, translationaler Forschung oder Programmmanagement im Biotech-Bereich unterstützen, indem Protein-Design-Projekte in nachverfolgbare Multi-Agenten-Pipelines überführt werden. Wahrscheinliche Anwendungsfälle sind automatisierte Überwachung von Publikationen, Zusammenfassungen zur Kandidatenbewertung, Normalisierung von Assay-Readouts und Reviews zur präklinischen Bereitschaft im Rahmen von HELIOPOLIS-BIOTECH-Projekten. In der Praxis könnte diese Kombination Teams in der therapeutischen Wirkstoffforschung dabei helfen, sich von fragmentierter Expertenkommunikation hin zu einem strukturierteren, auditierbaren Design-bis-Validierungs-Prozess zu bewegen.
Einbettungscode
Teile dieses KI-Tool auf deiner Website oder in deinem Blog, indem du den folgenden Code kopierst und einfügst. Das eingebettete Widget aktualisiert sich automatisch.
<iframe src="https://www.aimyflow.com/ai/heliopolistech-com/embed" width="100%" height="400" frameborder="0"></iframe>