10x Science: KI-native Software für Wissenschaftler
Dieses Tool bewerten
Durchschnittsbewertung
Gesamtstimmen
Wähle deine Bewertung (1-10):
Detailinformationen
Was
10x Science ist eine KI-native Softwareplattform für Proteincharakterisierung und Omics-Analyse. Laut der Seite ist sie für Wissenschaftler konzipiert, die mit komplexen Proteindaten arbeiten, insbesondere in Workflows mit Top-Down-, Middle-Down-, Targeted-Protein- und Peptide-Mapping-Analysen.
Das Produkt scheint als fortschrittliche Forschungssoftware für Proteintherapeutika- und Proteoform-Analysen positioniert zu sein, mit Schwerpunkt auf der skalierbaren Auflösung posttranslationaler Modifikationen, Sequenzvarianten und unbekannter Modifikationen. Es präsentiert sich außerdem als herstellerneutral und darauf ausgelegt, Reibungsverluste in Workflows durch native Dateiverarbeitung, lokale asynchrone Verarbeitung und Cloud-Datenbank-Streaming zu reduzieren.
Funktionen
- Proteoform-aufgelöste Analyse — Löst komplexe kombinatorische PTMs wie Glykosylierung auf und hilft Forschern, Proteinformen zu charakterisieren, die mit Standardansätzen möglicherweise übersehen werden.
- De-novo-Top-Down-Sequenzierung und Suche nach unbekannten Modifikationen — Unterstützt entdeckungsorientierte Workflows zur Identifizierung von Sequenzmerkmalen und Modifikationen, ohne sich ausschließlich auf vordefinierte Erwartungen zu stützen.
- KI-natives Peptide Mapping für Proteintherapeutika — Hilft dabei, die Zielidentität zu bestätigen, PTMs zu quantifizieren und unerwartete Sequenzvarianten in therapeutischen Proteinen zu erkennen.
- Unterstützung für Top-Down-, Middle-Down- und gezielte Workflows — Deckt mehrere Strategien der Proteinanalyse in einer Umgebung ab, was den Wechsel zwischen Tools bei Charakterisierungsaufgaben reduzieren kann.
- Herstellerneutrale Dateiunterstützung — Akzeptiert
.raw- und.mzML-Dateien ohne angegebene Notwendigkeit einer Dateikonvertierung, was die Einführung in Umgebungen mit gemischten Instrumenten vereinfachen kann. - Integrierte Organisation von Forschungsdaten — Umfasst Ansichten für Projekte, Suchbibliotheken, Proteoform-Familien und den Aufbau von Modifikationen, die eine strukturierte Analyse und Überprüfung experimenteller Ergebnisse unterstützen.
Hilfreiche Tipps
- Eignung für Ihren spezifischen Proteomik-Workflow validieren — Die Seite unterstützt stark Anwendungsfälle der Proteincharakterisierung, aber Teams sollten prüfen, ob ihre genauen Assay-Typen, Instrumente und Berichtsanforderungen abgedeckt sind.
- Erklärbarkeit für regulierte oder besonders kritische Forschungskontexte bewerten — Da das Produkt KI-native Analyse betont, sollten Käufer prüfen, wie Ergebnisse von Wissenschaftlern eingesehen, annotiert und verifiziert werden.
- Native Dateiverarbeitung mit echten Labordaten testen — Die Plattform beansprucht eine reibungsarme Datenaufnahme und Herstellerneutralität, daher sollte sich eine praktische Bewertung auf tatsächliche Rohdaten Ihrer Instrumente konzentrieren.
- Anwendungsfälle mit PTMs und Proteoform-Komplexität priorisieren — Der klarste differenzierende Mehrwert scheint in schwierigen Charakterisierungsproblemen wie Glykosylierung, unbekannten Modifikationen und Sequenzvariantenanalysen zu liegen.
- Erwartungen an Zusammenarbeit und Bereitstellung frühzeitig klären — Die Seite erwähnt lokale asynchrone Verarbeitung und Cloud-Datenbank-Streaming, daher sollten Teams während der Evaluierung operative Anforderungen, Datenflüsse und die IT-Eignung klären.
OpenClaw-Fähigkeiten
Innerhalb des OpenClaw-Ökosystems könnte 10x Science wahrscheinlich als spezialisierte Analyse-Engine für Workflows zur Proteincharakterisierung dienen. Mögliche OpenClaw-Fähigkeiten könnten Agenten umfassen, die Rohdaten aus der Massenspektrometrie vorsortieren, Proben in Top-Down- oder Peptide-Mapping-Workflows leiten, PTM-Ergebnisse zusammenfassen und strukturierte Experiment-Briefs für Forschungsteams erstellen. Die Seite nennt keine native OpenClaw-Integration, daher sollte dies eher als Gelegenheit zur Workflow-Gestaltung denn als bestätigte Produktfunktion betrachtet werden.
Diese Kombination könnte insbesondere in Biopharma-, Proteomik- und translationalen Forschungskontexten nützlich sein. Beispielsweise könnten OpenClaw-Agenten wahrscheinlich eingehende Experimentwarteschlangen überwachen, Proteoform-Befunde projektübergreifend vergleichen, unerwartete Sequenzvarianten zur Prüfung durch Wissenschaftler kennzeichnen und entscheidungsreife Zusammenfassungen für Programme zur Antikörper- oder Enzymcharakterisierung erstellen. In der Praxis könnte dies die Zeit der Forscher von der manuellen Datenverarbeitung hin zu Interpretation, Methodenoptimierung und Kandidatenbewertung verlagern.
Einbettungscode
Teile dieses KI-Tool auf deiner Website oder in deinem Blog, indem du den folgenden Code kopierst und einfügst. Das eingebettete Widget aktualisiert sich automatisch.
<iframe src="https://www.aimyflow.com/ai/10xscience-com/embed" width="100%" height="400" frameborder="0"></iframe>
Ähnliche Tools entdecken
Profluent
Profluent ist eine KI-gestützte Plattform für Proteindesign, die Biologieteams dabei unterstützt, neue Proteine und Geneditoren für Anwendungen in der Medizin, Landwirtschaft und bei industriellen Enzymen zu entwickeln. Für Molekularbiologen, Bioingenieure und Teams in der Arzneimittelforschung können KI-designte Proteine die Erforschung neuartiger therapeutischer und Geneditierungs-Kandidaten jenseits natürlicher Gerüste beschleunigen.
HELIOPOLIS BIOTECH – Proteindesign, Antikörperdesign
Heliopolis Biotech ist ein Unternehmen für Protein- und Antikörperdesign, das computergestützte Algorithmen und experimentelle Charakterisierung einsetzt, um Biotechnologie- und Arzneimittelforschungsteams bei der Entwicklung neuartiger therapeutischer Proteine, Binder und redesignter Proteine zu unterstützen. In der KI-gestützten therapeutischen F&E kann eine solche Plattform Proteiningenieuren und Forschern in der Wirkstoffentdeckung helfen, schneller vom molekularen Design zur präklinischen Kandidatenbewertung zu gelangen.

ProteinQure
ProteinQure ist ein Biotechnologieunternehmen im klinischen Stadium, das mit seiner KI-gestützten ProteinStudio-Plattform neuartige peptidbasierte Therapeutika und gewebespezifische Verabreichungssysteme entwickelt, vor allem für Teams in der Arzneimittelforschung und Biopharma-Partner, die Präzisionsmedikamente entwickeln. Für Fachleute aus der Onkologie und der translationalen Forschung kann sein computergestützter Ansatz für das Peptiddesign dazu beitragen, die Entwicklung zielgerichteter Therapien mit präziserer Wirkstoffabgabe zu beschleunigen.
Menten KI
Menten AI ist eine generative KI-Plattform für das Design von Peptid-Makrozyklus-Wirkstoffen, die Teams dabei unterstützt, Peptide für komplexe Zielstrukturen zu entwerfen und zu optimieren, hauptsächlich für Forscher in der Pharmaindustrie und Arzneimittelforschung. Für medizinische Chemiker und Teams aus der computergestützten Biologie kann sie die Entdeckung präklinischer Kandidaten beschleunigen, indem sie generative Modelle mit physikbasierten und quantenmechanischen Simulationen kombiniert.
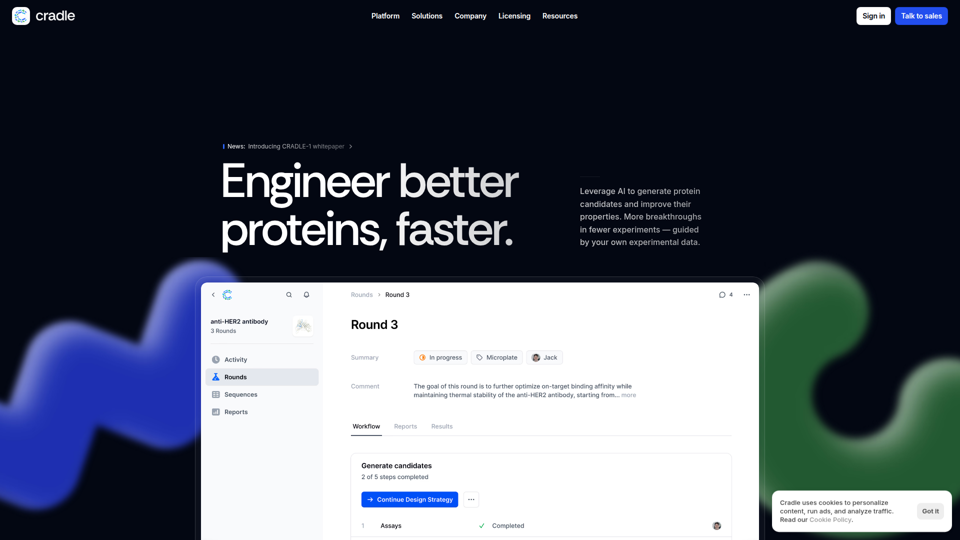
Wiege
Cradle ist eine KI-Plattform für Protein-Engineering, die Biopharma- und industrielle Bio-F&E-Teams dabei unterstützt, Proteinkandidaten mithilfe ihrer eigenen experimentellen Daten zu generieren und zu optimieren. Für Proteiningenieure und F&E-Wissenschaftler kann sie Design-Build-Test-Zyklen verkürzen, indem sie aus jeder Assay-Runde lernt, um eine schnellere Optimierung mehrerer Eigenschaften mit weniger Experimenten zu ermöglichen.
JURA Bio, Inc.
JURA Bio ist ein Biotechnologieunternehmen, das Grundlagenmodelle für das therapeutische Design entwickelt und Teams dabei unterstützt, Kandidaten zu entdecken und zu entwickeln, indem es KI-gestützte Nasslabor-Zyklen durchführt, die proprietäre funktionale Daten generieren – vor allem für Organisationen in der Arzneimittelforschung und therapeutischen F&E. Für Forschende in den Bereichen Biologika und frühe Entwicklungsphasen kann dieser KI-gesteuerte Labordatenkreislauf das Kandidatendesign für schwierige Targets und neuartige Modalitäten verbessern, bei denen öffentliche Datensätze und generische Modelle nur begrenzt verfügbar sind.
Antiverse: Entwicklung von Antikörpern für anspruchsvolle Targets
Antiverse ist eine durch maschinelles Lernen gestützte Plattform für das Antikörperdesign, die darauf ausgerichtet ist, Wirkstoffforschungsteams bei der Entwicklung von Antikörpern für anspruchsvolle Zielstrukturen in der therapeutischen Entwicklung zu unterstützen. In der KI-gestützten biologischen Forschung und Entwicklung kann dies Wissenschaftlern in der Antikörperforschung und Teams der computergestützten Biologie helfen, Kandidaten bei der Bearbeitung schwer adressierbarer Zielstrukturen effizienter zu priorisieren.

Erstellen:Biomedicines | Startseite
Generate:Biomedicines ist ein Therapeutika-Unternehmen, das maschinelles Lernen, biologische Verfahrenstechnik und Medizin über seine Generate-Plattform einsetzt, um neuartige proteinbasierte Arzneimittel zu entwerfen und zu entwickeln, hauptsächlich für Teams in der Arzneimittelforschung und Biopharmaindustrie. Für Forschende und Therapeutika-Entwickler kann dieser KI-gestützte generative Biologieansatz Design-Test-Zyklen verkürzen und eine gezieltere Protein-Entwicklung in der Arzneimittelentwicklung unterstützen.