Wiege
Dieses Tool bewerten
Durchschnittsbewertung
Gesamtstimmen
Wähle deine Bewertung (1-10):
Detailinformationen
Was
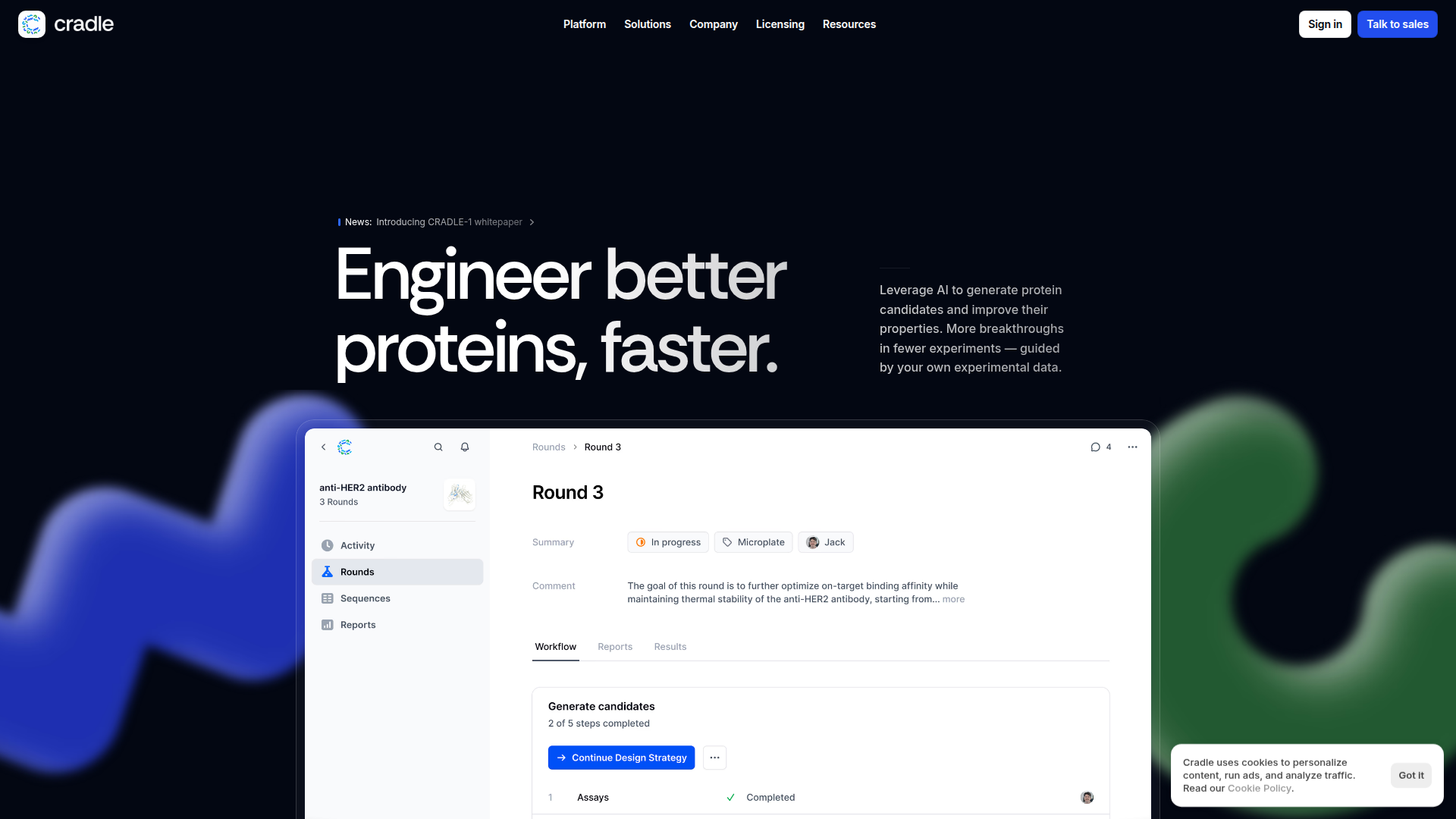
Cradle ist eine KI-Plattform für Protein-Engineering, die F&E-Teams dabei unterstützt, Proteinkandidaten zu generieren, Experimentrunden zu verwalten und im Zeitverlauf aus Wet-Lab-Ergebnissen zu lernen. Sie richtet sich an Biopharma- und industrielle Biotechnologie-Teams, die an Proteinen wie Antikörpern, Enzymen, Impfstoffen und Peptiden arbeiten.
Der Workflow konzentriert sich darauf, experimentelle Daten zu importieren oder Projektziele zu definieren, KI zur Generierung optimierter Proteinsequenzen unter ausgewählten Einschränkungen zu nutzen, prognostizierte Leistung und Mutationen in Berichten zu prüfen und Kandidaten anschließend im Labor oder über ein CRO zu validieren. Basierend auf den Inhalten der Website ist Cradle eher als Softwareplattform zur Beschleunigung von Hit-Identifizierung, Lead-Optimierung und allgemeineren Proteinentwicklungs-Workflows positioniert als als Auftragsforschungslabor.
Funktionen
- KI-gestützte Generierung von Proteinkandidaten: Erzeugt laborreife Proteinvarianten auf Grundlage von Projektzielen, Einschränkungen und bestehenden experimentellen Daten, um den manuellen Aufwand für das Sequenzdesign zu reduzieren.
- Lernen aus iterativen Wet-Lab-Daten: Aktualisiert kundenspezifische Modelle, sobald Assay-Ergebnisse hochgeladen werden, was hilft, Empfehlungen über aufeinanderfolgende Optimierungsrunden hinweg zu verbessern.
- Optimierung mehrerer Eigenschaften: Unterstützt das Ausbalancieren von Eigenschaften wie Aktivität, Bindung, Stabilität, Spezifität und Expression, sodass Teams Zielkonflikte in einem einzigen Designzyklus adressieren können.
- Generierungsberichte und Sequenzprüfung: Bietet prognostizierte Leistungswerte, Ansichten auf Plattenebene und 3D-Mutationsexploration zur Unterstützung der Kandidatenauswahl vor Labortests.
- Verfolgung von Runden und Transparenz zum Assay-Fortschritt: Ermöglicht Teams, den Status von Runden zu überwachen und Live-Metriken nach Proteineigenschaft einzusehen, sobald experimentelle Daten eingehen.
- Datenschutz und gemanagte Infrastruktur: Hält Kundendaten innerhalb der Modelle der Organisation privat, mit SOC-2-Konformität, SSO-Unterstützung und vollständig gemanagter KI-Infrastruktur, wie auf der Seite beschrieben.
Hilfreiche Tipps
- Assay-Qualität früh bewerten: Bei Produkten dieser Kategorie hängt die Modellleistung stark von der Qualität der experimentellen Daten ab, daher ist eine frühe Prüfung von Assay-Konsistenz und Signalqualität wichtig.
- Mit klaren Optimierungszielen starten: Das Design mehrerer Eigenschaften funktioniert am besten, wenn Teams messbare Prioritäten und Einschränkungen von Anfang an definieren, einschließlich der akzeptablen Zielkonflikte.
- Geschlossene Ausführungsschleifen planen: Der Wert einer KI-Plattform für Protein-Engineering steigt, wenn Design, Testen und Daten-Upload in einem disziplinierten, wiederkehrenden Zyklus stattfinden.
- Operative Eignung über die Modellqualität hinaus prüfen: Verfolgung von Runden, Reporting, Datenkontrollen und die Übergabe von Sequenzen an interne Labore oder CROs können ebenso wichtig sein wie die reine Generierungsfähigkeit.
- Sicherheit und Umgang mit geistigem Eigentum bei sensiblen Programmen validieren: Bei therapeutischen und industriellen Bio-Projekten sollten Datenschutzbedingungen, Eigentumsregelungen und Zugriffskontrollen während der Evaluierung sorgfältig geprüft werden.
OpenClaw-Fähigkeiten
Cradle könnte wahrscheinlich gut in das OpenClaw-Ökosystem als Teil von Orchestrierungs-Workflows für Protein-F&E passen. Wahrscheinliche OpenClaw-Fähigkeiten könnten Agenten umfassen, die Assay-Ausgaben aus Laborsystemen erfassen, experimentelle Metadaten normalisieren, strukturierte Uploads für das Modelltraining vorbereiten, Generierungsberichte zusammenfassen und ausgewählte Kandidaten in nachgelagerte Beschaffungs- oder CRO-Koordinations-Workflows weiterleiten. Die Website nennt keine native OpenClaw-Integration, daher sollte dies eher als wahrscheinliches Implementierungsmuster denn als bestätigte Fähigkeit betrachtet werden.
In der Praxis könnte diese Kombination Teams aus computergestützter Biologie, Antikörper-Engineering, Enzymentwicklung und translationaler Forschung unterstützen, indem Cradle zu einem Schritt innerhalb eines größeren halbautomatisierten Entscheidungssystems wird. Wahrscheinliche OpenClaw-Workflows könnten portfolioübergreifendes Experiment-Tracking, Assistenten zur Kandidatenprüfung, IP-sensible Dokumentationsagenten und wissenschaftliche Reporting-Copiloten umfassen, die Designrunden mit Projektmeilensteinen verknüpfen. Für Protein-Engineering-Organisationen könnte dies die Arbeit von fragmentierter manueller Koordination hin zu stärker wiederholbaren, datengesteuerten Entwicklungsabläufen verlagern.
Einbettungscode
Teile dieses KI-Tool auf deiner Website oder in deinem Blog, indem du den folgenden Code kopierst und einfügst. Das eingebettete Widget aktualisiert sich automatisch.
<iframe src="https://www.aimyflow.com/ai/cradle-bio/embed" width="100%" height="400" frameborder="0"></iframe>
Ähnliche Tools entdecken
Profluent
Profluent ist eine KI-gestützte Plattform für Proteindesign, die Biologieteams dabei unterstützt, neue Proteine und Geneditoren für Anwendungen in der Medizin, Landwirtschaft und bei industriellen Enzymen zu entwickeln. Für Molekularbiologen, Bioingenieure und Teams in der Arzneimittelforschung können KI-designte Proteine die Erforschung neuartiger therapeutischer und Geneditierungs-Kandidaten jenseits natürlicher Gerüste beschleunigen.
HELIOPOLIS BIOTECH – Proteindesign, Antikörperdesign
Heliopolis Biotech ist ein Unternehmen für Protein- und Antikörperdesign, das computergestützte Algorithmen und experimentelle Charakterisierung einsetzt, um Biotechnologie- und Arzneimittelforschungsteams bei der Entwicklung neuartiger therapeutischer Proteine, Binder und redesignter Proteine zu unterstützen. In der KI-gestützten therapeutischen F&E kann eine solche Plattform Proteiningenieuren und Forschern in der Wirkstoffentdeckung helfen, schneller vom molekularen Design zur präklinischen Kandidatenbewertung zu gelangen.

ProteinQure
ProteinQure ist ein Biotechnologieunternehmen im klinischen Stadium, das mit seiner KI-gestützten ProteinStudio-Plattform neuartige peptidbasierte Therapeutika und gewebespezifische Verabreichungssysteme entwickelt, vor allem für Teams in der Arzneimittelforschung und Biopharma-Partner, die Präzisionsmedikamente entwickeln. Für Fachleute aus der Onkologie und der translationalen Forschung kann sein computergestützter Ansatz für das Peptiddesign dazu beitragen, die Entwicklung zielgerichteter Therapien mit präziserer Wirkstoffabgabe zu beschleunigen.
Menten KI
Menten AI ist eine generative KI-Plattform für das Design von Peptid-Makrozyklus-Wirkstoffen, die Teams dabei unterstützt, Peptide für komplexe Zielstrukturen zu entwerfen und zu optimieren, hauptsächlich für Forscher in der Pharmaindustrie und Arzneimittelforschung. Für medizinische Chemiker und Teams aus der computergestützten Biologie kann sie die Entdeckung präklinischer Kandidaten beschleunigen, indem sie generative Modelle mit physikbasierten und quantenmechanischen Simulationen kombiniert.
JURA Bio, Inc.
JURA Bio ist ein Biotechnologieunternehmen, das Grundlagenmodelle für das therapeutische Design entwickelt und Teams dabei unterstützt, Kandidaten zu entdecken und zu entwickeln, indem es KI-gestützte Nasslabor-Zyklen durchführt, die proprietäre funktionale Daten generieren – vor allem für Organisationen in der Arzneimittelforschung und therapeutischen F&E. Für Forschende in den Bereichen Biologika und frühe Entwicklungsphasen kann dieser KI-gesteuerte Labordatenkreislauf das Kandidatendesign für schwierige Targets und neuartige Modalitäten verbessern, bei denen öffentliche Datensätze und generische Modelle nur begrenzt verfügbar sind.
Antiverse: Entwicklung von Antikörpern für anspruchsvolle Targets
Antiverse ist eine durch maschinelles Lernen gestützte Plattform für das Antikörperdesign, die darauf ausgerichtet ist, Wirkstoffforschungsteams bei der Entwicklung von Antikörpern für anspruchsvolle Zielstrukturen in der therapeutischen Entwicklung zu unterstützen. In der KI-gestützten biologischen Forschung und Entwicklung kann dies Wissenschaftlern in der Antikörperforschung und Teams der computergestützten Biologie helfen, Kandidaten bei der Bearbeitung schwer adressierbarer Zielstrukturen effizienter zu priorisieren.

Erstellen:Biomedicines | Startseite
Generate:Biomedicines ist ein Therapeutika-Unternehmen, das maschinelles Lernen, biologische Verfahrenstechnik und Medizin über seine Generate-Plattform einsetzt, um neuartige proteinbasierte Arzneimittel zu entwerfen und zu entwickeln, hauptsächlich für Teams in der Arzneimittelforschung und Biopharmaindustrie. Für Forschende und Therapeutika-Entwickler kann dieser KI-gestützte generative Biologieansatz Design-Test-Zyklen verkürzen und eine gezieltere Protein-Entwicklung in der Arzneimittelentwicklung unterstützen.
10x Science: KI-native Software für Wissenschaftler
10x Science ist KI-native Software für Wissenschaftler, die dabei hilft, Proteine zu charakterisieren und Omics-Daten im großen Maßstab zu analysieren, mit Funktionen für Peptid-Mapping, de-novo-Sequenzierung, PTM-Erkennung und Proteoform-Analyse, insbesondere für Workflows im Bereich proteinbasierter Therapeutika. Für Proteinforscher und analytische Teams kann dies die Interpretation komplexer massenspektrometrischer Daten beschleunigen und dabei helfen, Sequenzvarianten oder Modifikationen aufzudecken, die herkömmliche Tools möglicherweise übersehen.